Generating long deletions across the genome with pooled paired prime editing screens
通过 Twin-PE 技术实现超长片段的精准删除,最长可高效删除 Mb 基因
英国帝国理工学院威康桑格研究所 Leopold Parts1 团队在预印本发表“Generating long deletions across the genome with pooled paired prime editing screens”文章。
蛋白质编码区仅占基因组的不到 2%,其余非编码 DNA 中高达 10% 的部分参与调控和结构功能,包括增强子、启动子、非编码 RNA 以及染色质相关元件,其中许多在发育过程和疾病生成有很大关系。但对非编码的功能功能的直接验证仍然有限,有时只能采用迂回策略或者反向验证方法,部分原因是我们缺乏能够精准且可扩展地操纵大片段基因组的高通量工具。虽然通过 Cas-dual-sgRNA 可以实现大片段的删除,但是远远不能做到精准基因删除,且 DSB 会产生细胞毒性,dual-sgRNA 增加脱靶,染色体异常等问题。而通过 CRISPRi,CRISPRoff、siRNA 干扰等方法只能调控非编码区或者 RNA 表达,只能降低非编码 RNA 表达,无法完全 KO 敲除。
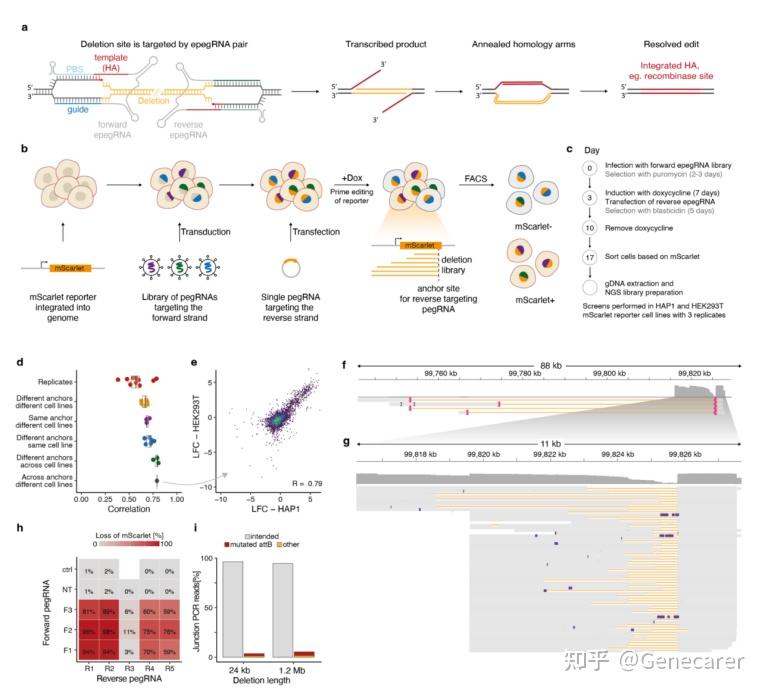
图 1:采用配对先导编辑技术开展高通量缺失筛选。首先在 mScarlet 模型系统中验证该方法的能力,在 hap1 和 HEK293 细胞系中成功构建超过 3,800 个长达 1.2 兆碱基的缺失。揭示了先导缺失效率的关键决定因素,包括缺失长度、先导编辑 pegRNA 效能,并运用这些发现构建了杜氏肌营养不良症和色素性视网膜炎疾病模型中具有临床意义的缺失突变。进一步构建了覆盖 149 个基因、超过 10,000 处缺失的全基因组规模筛选,阳性对照召回率达到约 72%,并鉴定出数百个影响细胞适应性的非基因区与非编码区域。
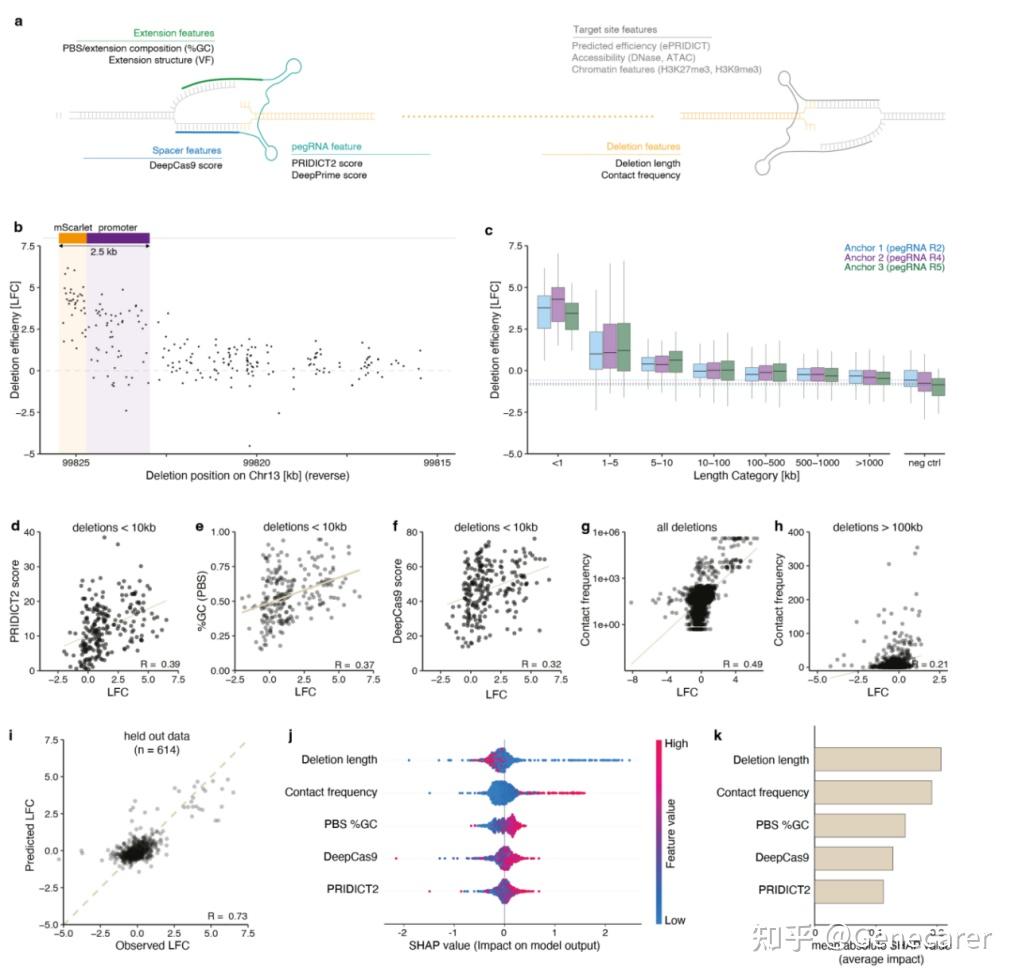
图 2:为了搞清楚片段缺失效率的决定因素,文章探究 pegRNA 设计特征的影响,包括 sgRNA,TRR 以及 PBS 特征。缺失片段的越大,编辑效率越低。缺失<1Kb 效率最高,缺失 1-5kb 效率中等,缺失 5-10Kb 只能检测到部分信号,而 100Kb 的缺失虽与阴性对照组差异较小但也具统计学显著性。最终发现较高的编辑效率与更优的 PRIDICT2 评分、DeepCas9 评分以及 PBS 区的 RNA 引物结合区的 GC 含量呈正相关。这一现象可能反映了逆转录同源臂在小距离范围内更易退火的技术偏好性,以及在开放且活跃转录的基因组环境中进行编辑的相对便利
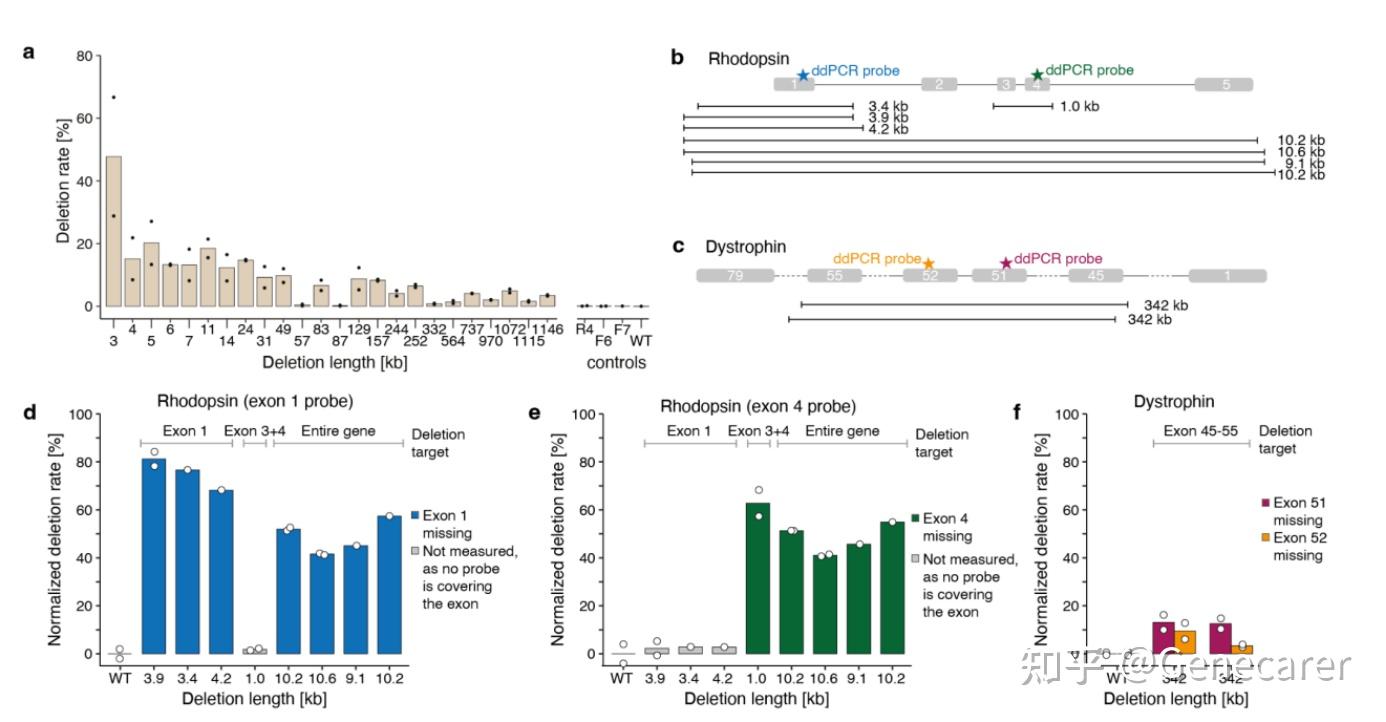
图 3:选取了 24 个高效的正向 pegRNA,尝试用固定的反向 pegRNA 分别删除报告基因中 3kb-1Mb 片段。其中 3kb 缺失实现了最高的编辑效率(48%),252kb 碱基的缺失效率也有 6.5%,而>1Mb 缺失效率分别为 4.9%、1.6% 和 3.5%。表明 Kb 级别碱基缺失效率较高,而 Mb 级别碱基效率低,但也可以实现。之后通过 3 组 Twin-Pe 分别删除单个外显子和完整的 RHO 基因,ddPCR 检测编辑效率,3.4-4.2kb 碱基缺失效率高达 84%,而以 9.1-10.6kb 碱基缺失的概率达 50%。
文章得出结论:Twin- PE 可实现无 DBS 的大片段删除,编辑效率高达 95%。可以用于在全基因范围内编辑目的基因外显子,内含子,5UTR,3UTR 等。 并可用于临床疾病大片段删除,如 RHO,DMD 基因等。